胃癌单细胞数据集GSE163558复现(二):Seurat V5标准流程
胃癌单细胞数据集GSE163558复现(二):Seurat V5标准流程
生信技能树jimmy
发布于 2024-06-13 18:24:19
发布于 2024-06-13 18:24:19
分享是一种态度

前言
Hello小伙伴们大家好,我是生信技能树的小学徒”我才不吃蛋黄“。今天是胃癌单细胞数据集GSE163558复现系列第二期。第一期我们进行了数据的下载与读取并成功构建Seurat对象。本期,我们将在第一期基础上走Seurat V5标准流程,对Seurat对象进行QC质控、并利用harmony整合去批次、并按标准流程进行降维聚类分群。
1质控
质控(quality control, QC)的目的是为了去除质量较差细胞,低质量的细胞会形成独特的亚群,使分群结果变得复杂;在主成分分析过程中,前几个主要成分将捕获质量差异而不是生物学差异,从而降低降维效果。因此,低质量的细胞可能会导致下游分析出现误导性结果。为了避免上述情况的发生,我们需要在下游分析开始前排除掉这些低质量细胞。
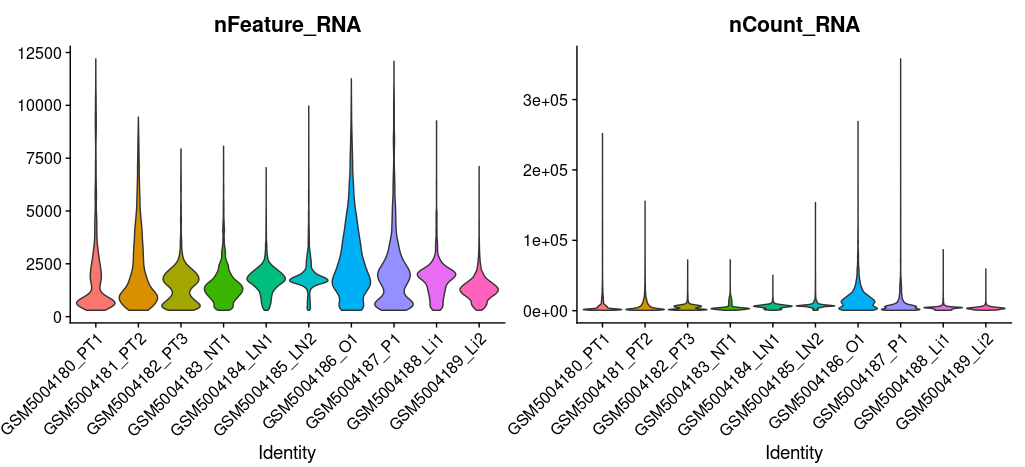
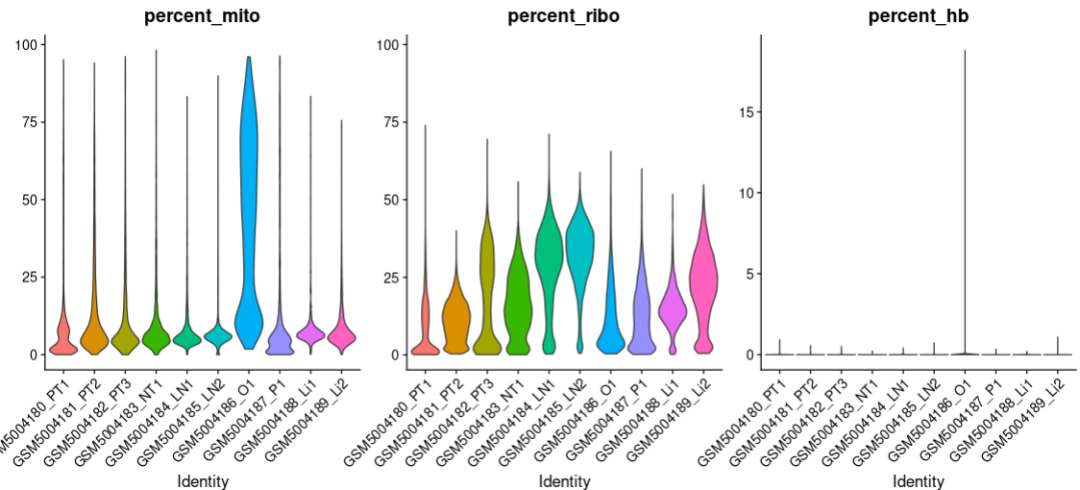
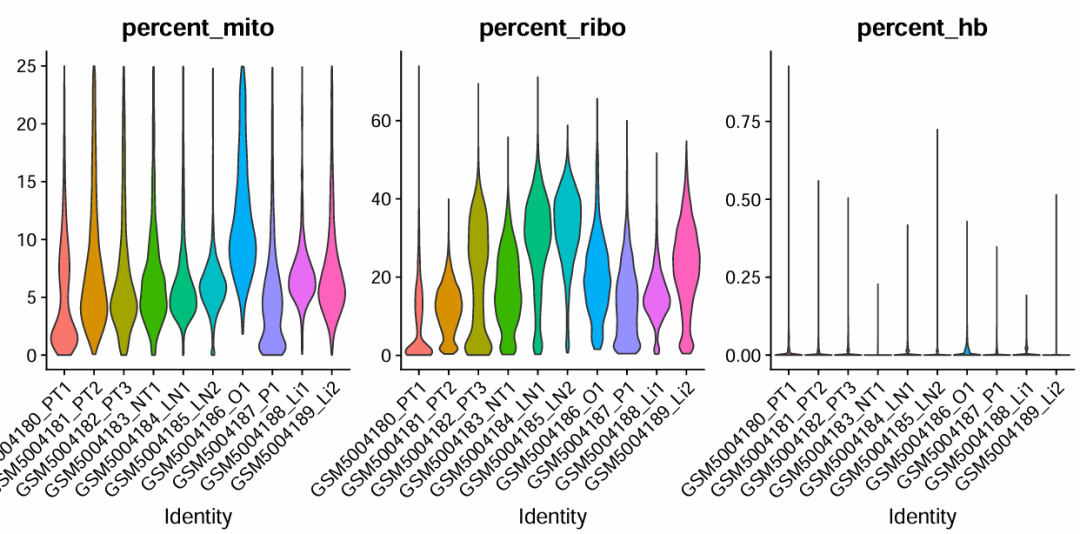
QC主要的指标有nCount_RNA(每个细胞的UMI数目)和nFeature_RNA(每个细胞中检测到的基因数量)以及"percent_mito"(表示细胞中线粒体基因的比例)这三个指标。此外,还可以纳入”percent_ribo“(核糖体基因比例)和”percent_hb“(红血细胞基因比例)两个指标。
细胞的UMI分子数和基因数反映细胞的质量,数量太低可能是细胞碎片,太高则可能是两个或多个细胞结团的情况;线粒体基因高表达的细胞,可能是处于凋亡状态或者裂解状态的细胞;核糖体基因高表达的细胞,细胞内出现RNA降解时;血红蛋白基因高表达的细胞通常为红细胞,而红细胞本身是不含有细胞核的,且携带的基因少,其携带的基因与疾病以及生物发育等过程没有太大的联系,所以可以直接剔除掉。
在这里,我们要利用PercentageFeatureSet函数分别计算每个细胞的"percent_mito",”percent_ribo“和”percent_hb“。首先加载R包,导入第一期生成的Seurat数据:
getwd()
setwd("")
rm(list=ls())
options(stringsAsFactors = F)
library(Seurat)
library(ggplot2)
library(clustree)
library(cowplot)
library(data.table)
library(dplyr)
sce.all <- readRDS("GSE163558.rds")
然后开始计算线粒体基因比例:
#计算线粒体基因比例
mito_genes=rownames(sce.all)[grep("^MT-", rownames(sce.all),ignore.case = T)]
print(mito_genes) #可能是13个线粒体基因,小鼠数据基因名为小写"^mt-"
#sce.all=PercentageFeatureSet(sce.all, "^MT-", col.name = "percent_mito")
sce.all=PercentageFeatureSet(sce.all, features = mito_genes, col.name = "percent_mito")
fivenum(sce.all@meta.data$percent_mito)
计算核糖体基因比例
#计算核糖体基因比例
ribo_genes=rownames(sce.all)[grep("^Rp[sl]", rownames(sce.all),ignore.case = T)]
print(ribo_genes)
sce.all=PercentageFeatureSet(sce.all, features = ribo_genes, col.name = "percent_ribo")
fivenum(sce.all@meta.data$percent_ribo)
再计算红血细胞基因比例
#计算红血细胞基因比例
Hb_genes=rownames(sce.all)[grep("^Hb[^(p)]", rownames(sce.all),ignore.case = T)]
print(Hb_genes)
sce.all=PercentageFeatureSet(sce.all, features = Hb_genes,col.name = "percent_hb")
fivenum(sce.all@meta.data$percent_hb)
head(sce.all@meta.data)
可视化细胞的上述比例情况
feats <- c("nFeature_RNA", "nCount_RNA", "percent_mito",
"percent_ribo", "percent_hb")
feats <- c("nFeature_RNA", "nCount_RNA")
p1=VlnPlot(sce.all, group.by = "orig.ident", features = feats, pt.size = 0, ncol = 2) +
NoLegend()
p1
w=length(unique(sce.all$orig.ident))/3+5;w
ggsave(filename="Vlnplot1.pdf",plot=p1,width = w,height = 5)
feats <- c("percent_mito", "percent_ribo", "percent_hb")
p2=VlnPlot(sce.all, group.by = "orig.ident", features = feats, pt.size = 0, ncol = 3, same.y.lims=T) +
scale_y_continuous(breaks=seq(0, 100, 5)) +
NoLegend()
p2
w=length(unique(sce.all$orig.ident))/2+5;w
ggsave(filename="Vlnplot2.pdf",plot=p2,width = w,height = 5)
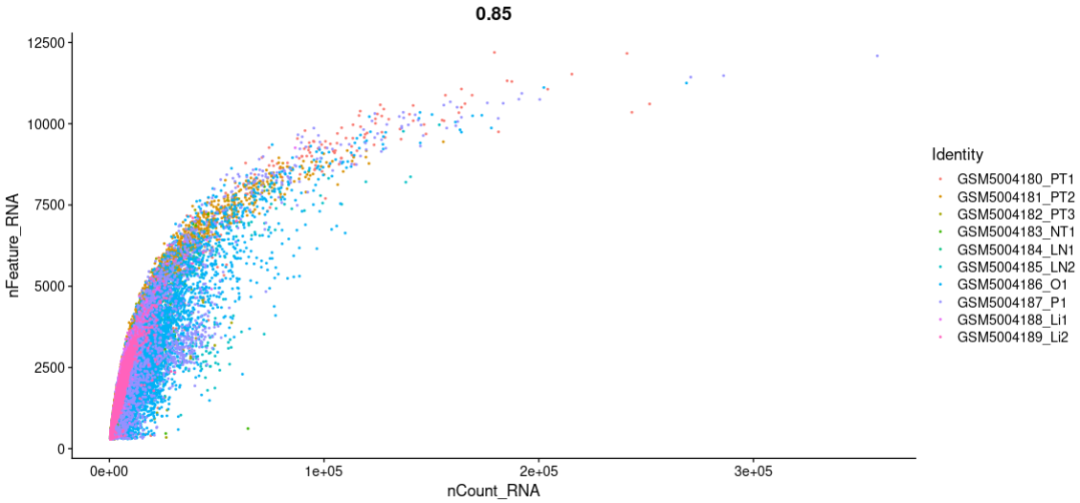
p3=FeatureScatter(sce.all, "nCount_RNA", "nFeature_RNA", group.by = "orig.ident", pt.size = 0.5)
p3
ggsave(filename="Scatterplot.pdf",plot=p3)
结果如下:
p1:nCount_RNA与nFeature_RNA
p2:"percent_mito",”percent_ribo“和”percent_hb“
p3:nCount_RNA与nFeature_RNA相关性分析
根据上述指标,过滤低质量细胞/基因
过滤指标1:最少表达基因数的细胞 and 最少表达细胞数的基因
一般来说,在CreateSeuratObject的时候已经是进行了这个过滤操作,如果后期看到了自己的单细胞降维聚类分群结果很诡异,就可以回过头来看质量控制环节,先走默认流程即可。
if(F){
selected_c <- WhichCells(sce.all, expression = nFeature_RNA > 500)
selected_f <- rownames(sce.all)[Matrix::rowSums(sce.all@assays$RNA$counts > 0 ) > 3]
sce.all.filt <- subset(sce.all, features = selected_f, cells = selected_c)
dim(sce.all)
dim(sce.all.filt)
}
sce.all.filt = sce.all
# par(mar = c(4, 8, 2, 1))
# 这里的C 这个矩阵,有一点大,可以考虑随抽样
C=subset(sce.all.filt,downsample=100)@assays$RNA$counts
dim(C)
C=Matrix::t(Matrix::t(C)/Matrix::colSums(C)) * 100
most_expressed <- order(apply(C, 1, median), decreasing = T)[50:1]
pdf("TOP50_most_expressed_gene.pdf",width=14)
boxplot(as.matrix(Matrix::t(C[most_expressed, ])),
cex = 0.1, las = 1,
xlab = "% total count per cell",
col = (scales::hue_pal())(50)[50:1],
horizontal = TRUE)
dev.off()
rm(C)
过滤指标2:线粒体/核糖体基因比例(根据上面的violin图)
这里,我们筛选的标准是:percent_mito < 25,percent_ribo > 3,percent_hb < 1。不同的数据集,不同的组织,需要根据特定情况来调整筛选阈值。
selected_mito <- WhichCells(sce.all.filt, expression = percent_mito < 25)
selected_ribo <- WhichCells(sce.all.filt, expression = percent_ribo > 3)
selected_hb <- WhichCells(sce.all.filt, expression = percent_hb < 1 )
length(selected_hb)
length(selected_ribo)
length(selected_mito)
sce.all.filt <- subset(sce.all.filt, cells = selected_mito)
sce.all.filt <- subset(sce.all.filt, cells = selected_ribo)
sce.all.filt <- subset(sce.all.filt, cells = selected_hb)
dim(sce.all.filt)
table(sce.all.filt$orig.ident)
length(sce.all.filt$orig.ident)
我们再统计一下QC前后各样本细胞数:
第一期QC前各样本细胞数:

本期QC后各样本细胞数:

可以看到,QC后细胞数量由53093个变成45548个,过滤成功(特别是GSM5004186_O1这个样本,很多细胞线粒体基因的含量较高,未过滤前有5837个细胞,过滤掉低质量的细胞之后,剩下1909个)。
可视化过滤后的情况:
feats <- c("nFeature_RNA", "nCount_RNA")
p1_filtered=VlnPlot(sce.all.filt, group.by = "orig.ident", features = feats, pt.size = 0, ncol = 2) +
NoLegend()
w=length(unique(sce.all.filt$orig.ident))/3+5;w
ggsave(filename="Vlnplot1_filtered.pdf",plot=p1_filtered,width = w,height = 5)
feats <- c("percent_mito", "percent_ribo", "percent_hb")
p2_filtered=VlnPlot(sce.all.filt, group.by = "orig.ident", features = feats, pt.size = 0, ncol = 3) +
NoLegend()
w=length(unique(sce.all.filt$orig.ident))/2+5;w
ggsave(filename="Vlnplot2_filtered.pdf",plot=p2_filtered,width = w,height = 5)
p1_filtered
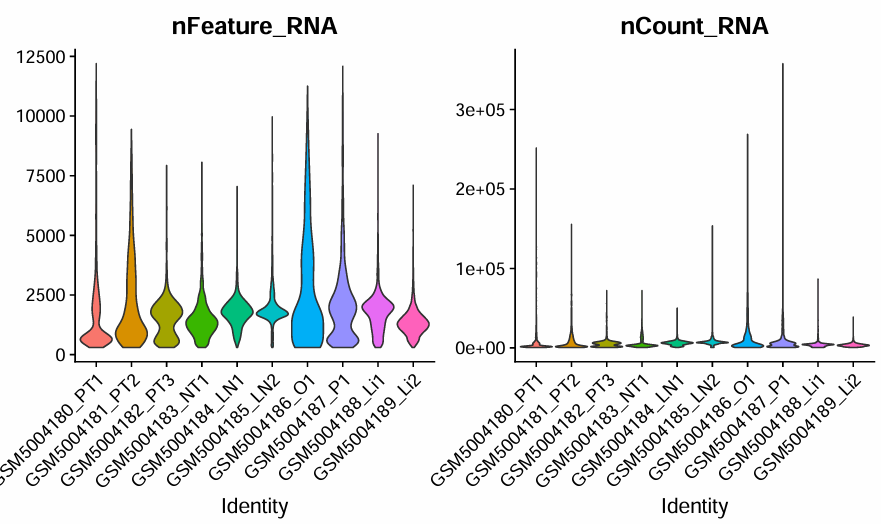
p2_filtered
2 harmony整合多个单细胞样品
细胞筛选之后,我们需要进行harmony整合。第一期我们在创建总的Seurat对象时,使用了merge函数对多个Seurat进行了简单的合并。merge只是按照行和列进行了合并,并未对数据进行其他处理。

在拿到下游单细胞矩阵前,样本经历了多个实验环节的处理,时间、处理人员、试剂以及技术平台等变量都会成为混杂因素。以上因素混合到一起,就会导致数据产生批次效应(batch effect)。为了尽可能避免混杂因素,我们可以严格把控测序的技术流程,同时也需要在下游分析中进行事后补救(算法去批次)。目前单细胞测序常用的去批次算法有Harmony,CCA,RPCA,FastMNN,scVI等。在这里,我们采用Harmony进行演示。
在Harmony去批次前,我们需要进行以下流程:
数据标准化
数据标准化的方法是通过对原始表达值进行对数转换"LogNormalize",使其总体更加符合正态分布。经过对数转换之后,不同基因或细胞之间也更具有可比性,从一定程度上消除不同细胞之间的技术差异。
sce.all.filt <- NormalizeData(sce.all.filt,
normalization.method = "LogNormalize",
scale.factor = 1e4)
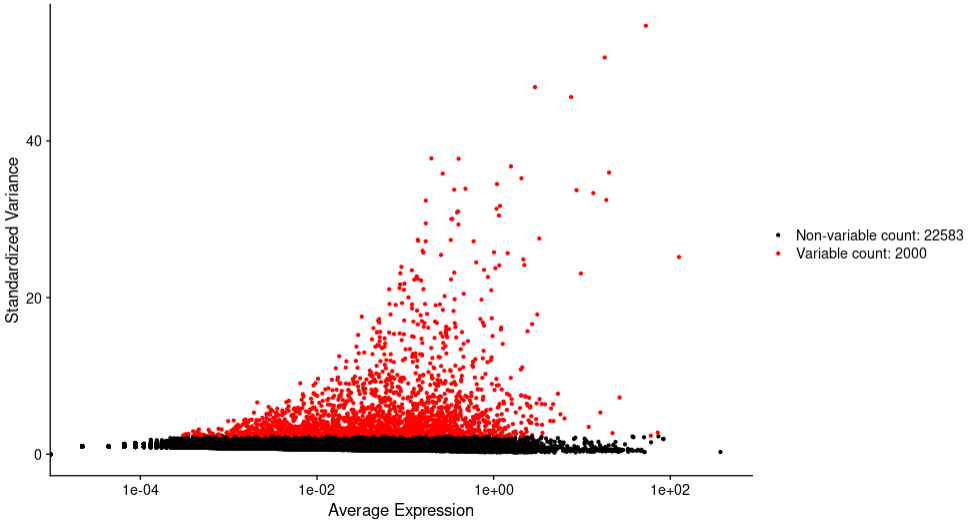
筛选高变基因
高变异基因就是highly variable features(HVGs)是指在某些细胞中高度表达,而在其他细胞中低度表达的基因。默认情况下,此步骤回筛选2000个HVGs用于下游分析。
sce.all.filt <- FindVariableFeatures(sce.all.filt)
p4 <- VariableFeaturePlot(sce.all.filt)
p4
高变基因
数据归一化
scale归一化:将每个基因在所有细胞中的均值变为0,方差标为1,赋予每个基因在下游分析中同样的权重,不至于使高表达基因占据主导地位
sce.all.filt <- ScaleData(sce.all.filt)
PCA线性降维
单细胞测序是一种高通量测序技术,它产生的数据集在细胞和基因数量上都具有很高的维度。这立即指向了一个事实,即单细胞测序数据受到了"维度诅咒"的困扰(单细胞最好的教程(四):降维)。
"维度诅咒"这个概念最早是由R. Bellman提出的,它描述的是理论上高维数据包含更多的信息,但在实践中并非如此。更高维度的数据往往包含更多的噪声和冗余,因此增加更多的信息并不利于后续的分析步骤。
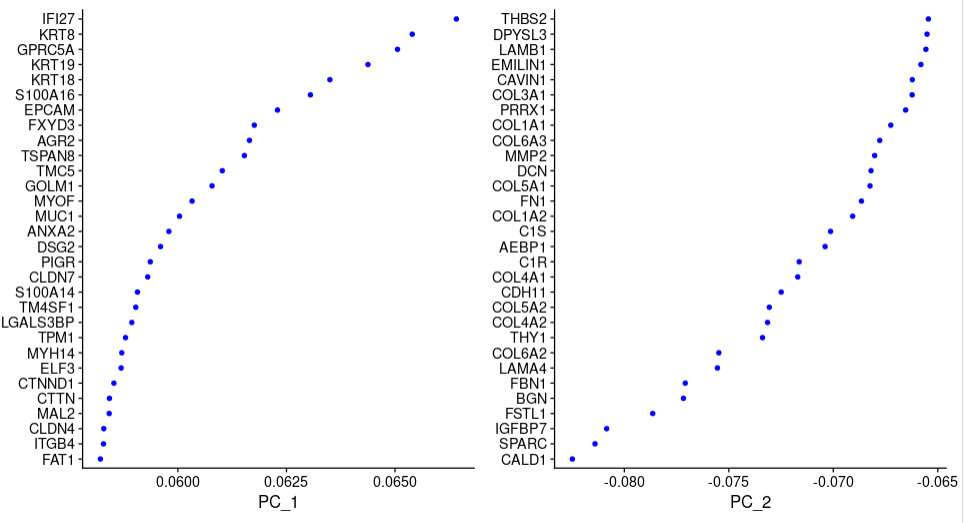
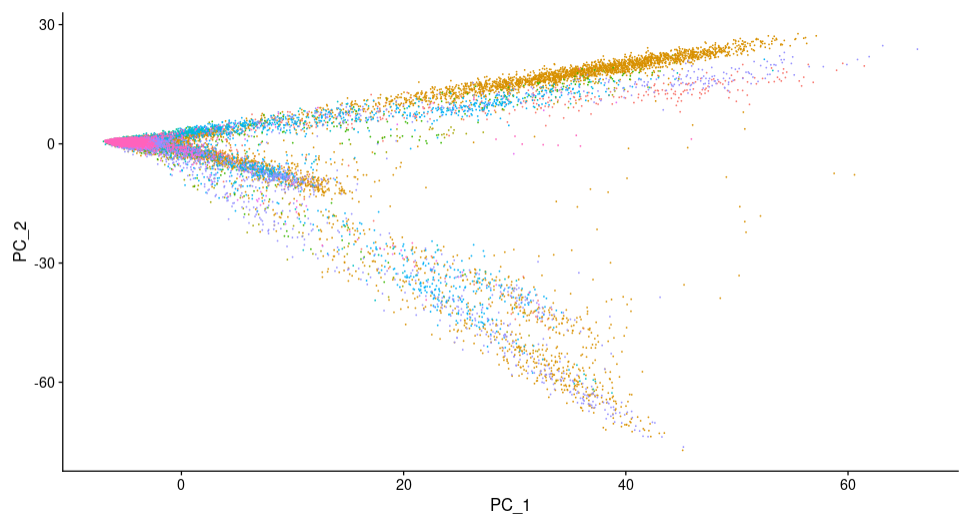
为了在数据的处理和可视化更加便捷的同时,保留数据重要的信息,在这里我们需要应用PCA(principal components analysis)即主成分分析技术,降低数据维度(单细胞PCA降维结果理解)。
sce.all.filt <- RunPCA(sce.all.filt, features = VariableFeatures(object = sce.all.filt))
##可视化PCA结果
VizDimLoadings(sce.all.filt, dims = 1:2, reduction = "pca")
DimPlot(sce.all.filt, reduction = "pca") + NoLegend()
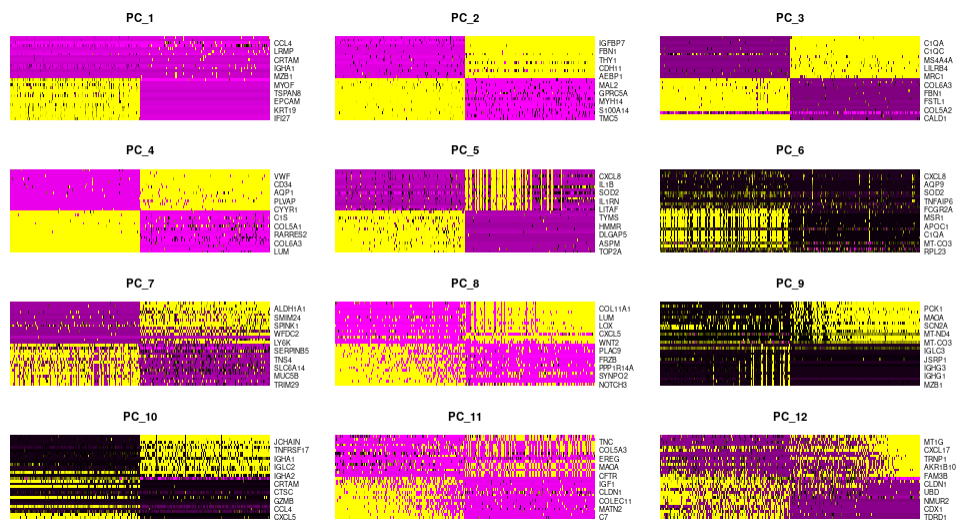
DimHeatmap(sce.all.filt, dims = 1:12, cells = 500, balanced = TRUE)
PCA可视化结果
Harmony去批次
seuratObj <- RunHarmony(sce.all.filt, "orig.ident")
names(seuratObj@reductions)
[1] "pca" "harmony"
我们可以看到,RunHarmony后,Harmony的结果已经在seuratObj的reductions中。
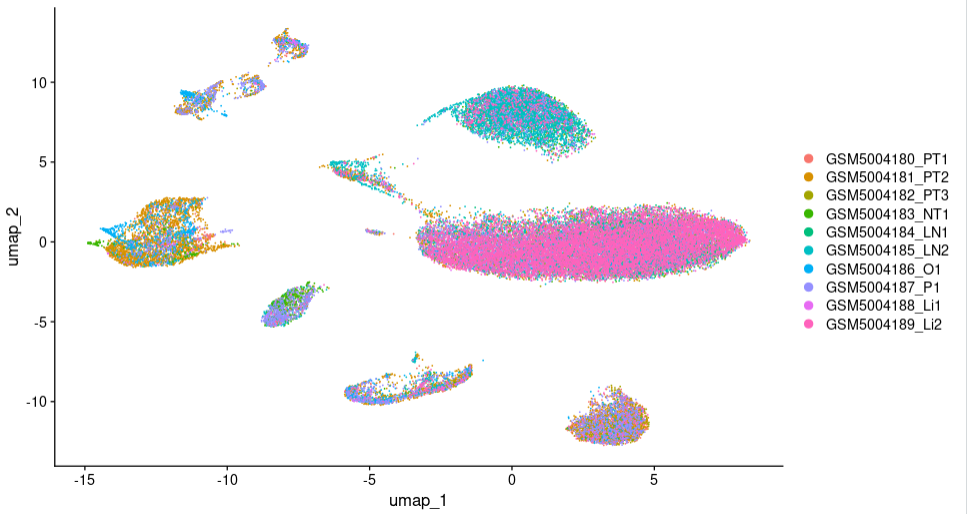
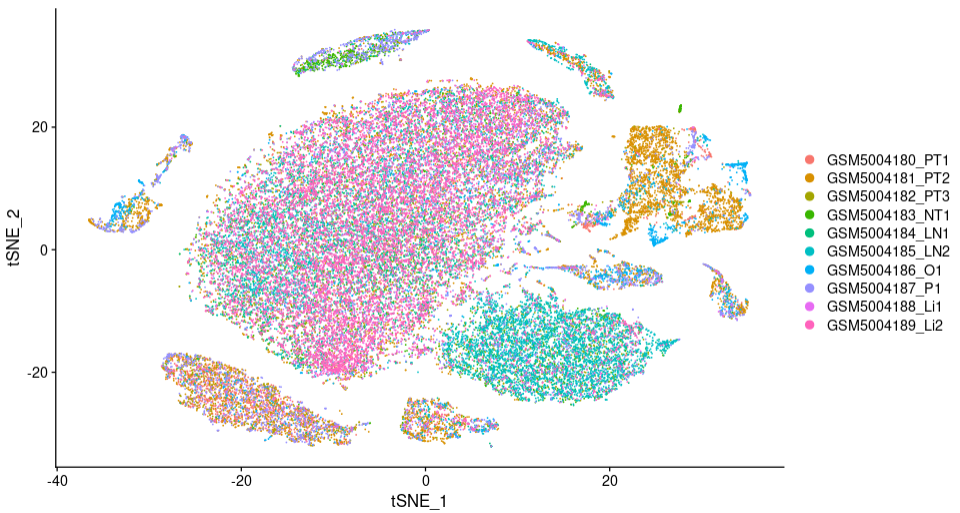
然后使用UMAP/TSNE可视化Harmony去批次效果:
seuratObj <- RunUMAP(seuratObj, dims = 1:15,
reduction = "harmony")
DimPlot(seuratObj,reduction = "umap",label=F )
seuratObj <- RunTSNE(seuratObj, dims = 1:15,
reduction = "harmony")
DimPlot(seuratObj,reduction = "tsne",label=F )
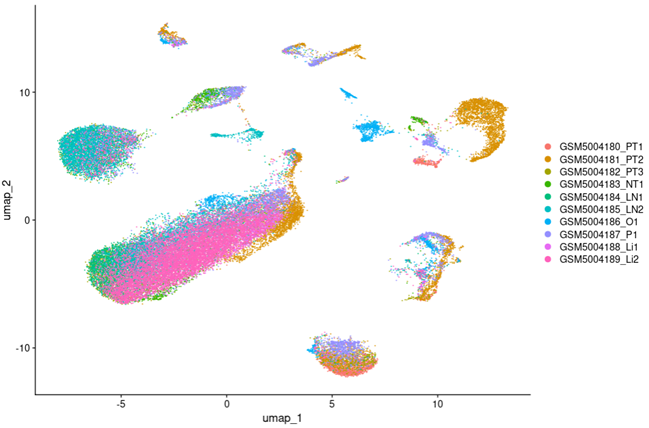
UMAP1
TSNE1
我们再来看一下不用Harmony去批次的效果:
UMAP2
TSNE2
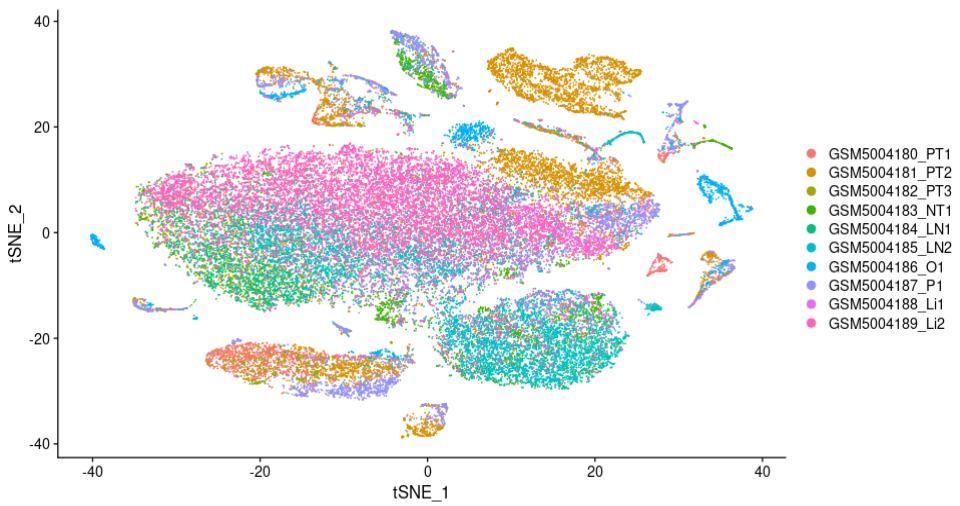
两组图对比我们可以看到,运行Harmony后,各样本散点融合的更好,表明该数据集需要去批次且Harmony去批次效果较好。
3 细胞聚类
Seurat软件使用基于图论的聚类算法对细胞进行聚类和分群,要包括以下步骤:
- 1.构建细胞间的聚类关系:利用PCA空间中的欧几里得距离构建KNN聚类关系图;
- 2.优化细胞间聚类关系距离的权重值:利用Jaccard相似性优化任意两个细胞间的边缘权重;
- 3.聚类和分群:使用Louvain 算法进行细胞群聚类优化。
分群标准的确定使用了两个函数FindNeighbors和FindClusters。
FindNeighbors函数用于计算给定数据集的最近邻图,可以返回包含KNN和SNN的对象列表。还可以通过迭代分组来优化聚类结果,以最大化标准模块度函数。
FindClusters函数是基于共享最近邻(SNN)模块化优化的聚类算法识别细胞簇。该函数的重要参数为分辨率resolution,resolution最小值为0,分为1类;值越大,分群数越多;在0.4-1.2之间通常会对3k 左右的单细胞数据集产生良好的结果。
我们先运行FindNeighbors:
sce.all.filt=seuratObj
sce.all.filt <- FindNeighbors(sce.all.filt, reduction = "harmony",
dims = 1:15)
sce.all.filt.all=sce.all.filt
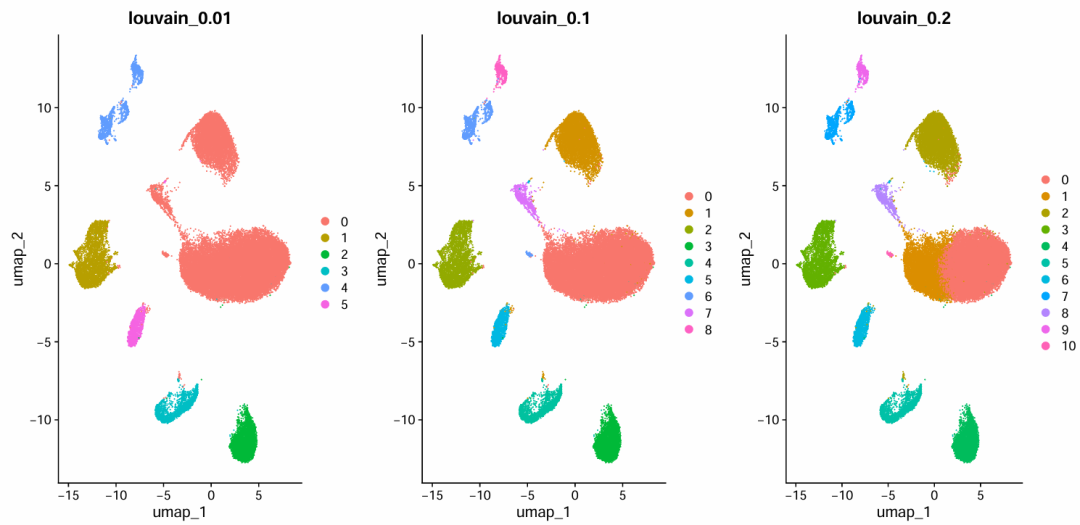
然后再运行FindClusters,在这里我们使用了for循环,设置了不同的分辨率,观察分群效果。
#设置不同的分辨率,观察分群效果(选择哪一个?)
for (res in c(0.01, 0.05, 0.1, 0.2, 0.3, 0.5,0.8,1)) {
sce.all.filt.all=FindClusters(sce.all.filt.all, #graph.name = "CCA_snn",
resolution = res, algorithm = 1)
}
colnames(sce.all.filt.all@meta.data)
apply(sce.all.filt.all@meta.data[,grep("RNA_snn",colnames(sce.all.filt.all@meta.data))],2,table)
p1_dim=plot_grid(ncol = 3, DimPlot(sce.all.filt.all, reduction = "umap", group.by = "RNA_snn_res.0.01") +
ggtitle("louvain_0.01"), DimPlot(sce.all.filt.all, reduction = "umap", group.by = "RNA_snn_res.0.1") +
ggtitle("louvain_0.1"), DimPlot(sce.all.filt.all, reduction = "umap", group.by = "RNA_snn_res.0.2") +
ggtitle("louvain_0.2"))
ggsave(plot=p1_dim, filename="Dimplot_diff_resolution_low.pdf",width = 14)
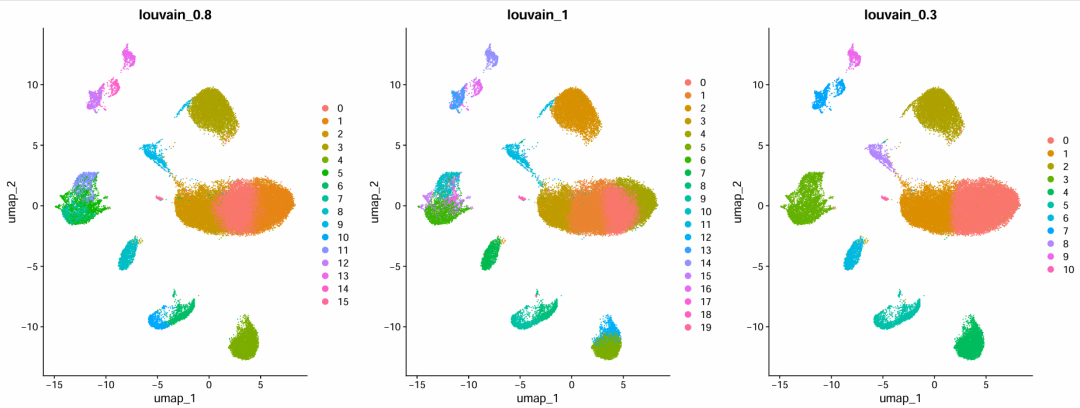
p1_dim=plot_grid(ncol = 3, DimPlot(sce.all.filt.all, reduction = "umap", group.by = "RNA_snn_res.0.8") +
ggtitle("louvain_0.8"), DimPlot(sce.all.filt.all, reduction = "umap", group.by = "RNA_snn_res.1") +
ggtitle("louvain_1"), DimPlot(sce.all.filt.all, reduction = "umap", group.by = "RNA_snn_res.0.3") +
ggtitle("louvain_0.3"))
ggsave(plot=p1_dim, filename="Dimplot_diff_resolution_high.pdf",width = 18)
p2_tree=clustree(sce.all.filt.all@meta.data, prefix = "RNA_snn_res.")
ggsave(plot=p2_tree, filename="Tree_diff_resolution.pdf")
table(sce.all.filt.all@active.ident)
可视化分群效果
Dimplot_diff_resolution_low
Dimplot_diff_resolution_high
Tree_diff_resolution
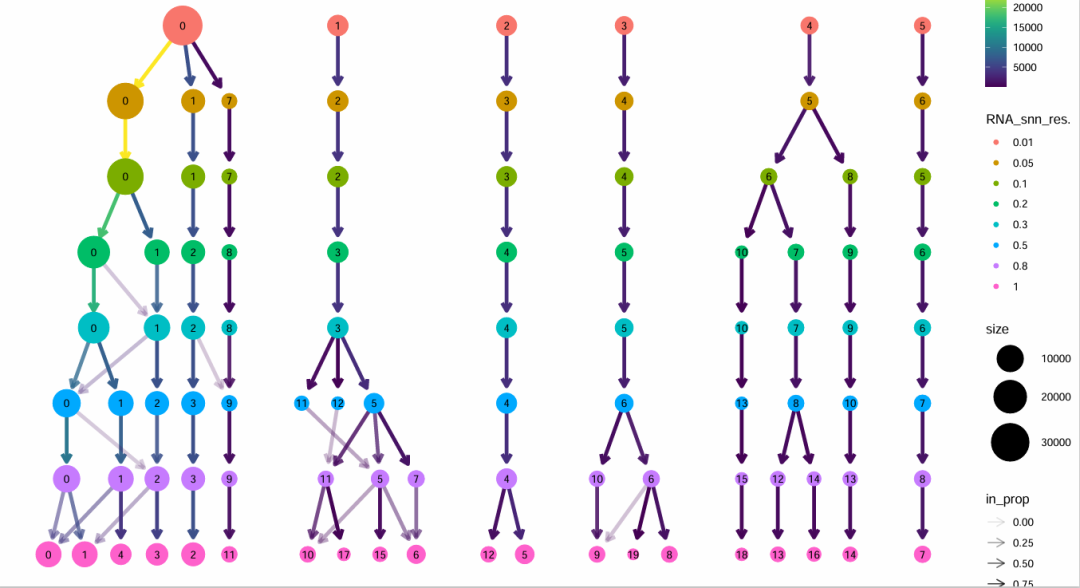
结语
本期,我们介绍了Seurat V5标准流程,对Seurat对象进行QC质控、并利用harmony整合去批次、并按标准流程进行降维聚类分群。下一期,我们将在此基础上选择resolution=0.5对细胞进行分群注释,欢迎大家持续追更,谢谢!
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2024-06-07,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

