比较pls包中PCR函数中的所有变量,R
比较pls包中PCR函数中的所有变量,R
提问于 2017-08-25 01:47:34
我试图在R中进行主成分回归分析( PCR ),通常我会做主成分分析( PCA ),但是我有多重共线性,并且读到PCR可以处理这个问题。
我正在使用来自pcr包的pls函数。这需要一个公式来识别要比较的变量。我希望能够比较每个变量和其他变量,就像PCA一样。但是,在这个函数中,我只能知道如何将一个变量与每个其他变量进行比较,并且取决于我选择的变量,结果会发生变化。当然,我可能没有正确理解PCR。
下面是一个使用iris数据集的示例。
library(pls)
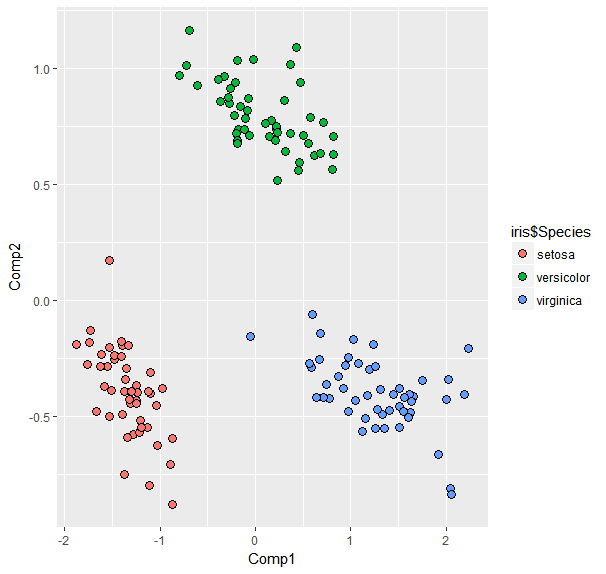
library(ggplot2)将Petal.Length与所有其他变量进行比较:
ir.pcr<-pcr(Petal.Length~ ., data = iris, validation = "CV")#PCR comparing `Petal.Length` with all other variables
df<-data.frame(ir.pcr$scores[,1],ir.pcr$scores[,2])#get first 2 COMP scores from PCR for ggplot
colnames(df)<-c('Comp1', 'Comp2')
ggplot(data=df,aes(x=Comp1,y=Comp2)) +
geom_point(aes(fill=iris$Species),shape=21,colour='black',size=3)#plot points
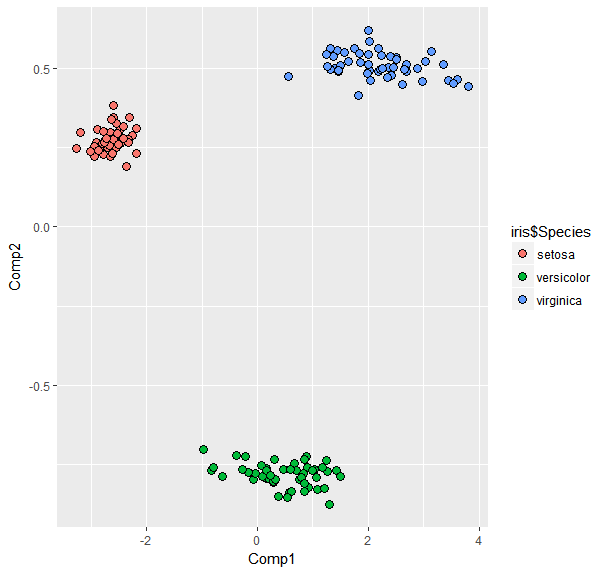
与其他变量相比,使用Sepal.Width:
ir.pcr<-pcr(Sepal.Width~ ., data = iris, validation = "CV")#PCR
df<-data.frame(ir.pcr$scores[,1],ir.pcr$scores[,2])#get first 2 COMP scores from PCR for ggplot
colnames(df)<-c('Comp1', 'Comp2')
ggplot(data=df,aes(x=Comp1,y=Comp2)) +
geom_point(aes(fill=iris$Species),shape=21,colour='black',size=3)#plot points
我的理解是,在公式中包含.后的~意味着“与其他所有事物相比”。如果是这样的话,那么我怎样才能让.~.能够将每个变量与其他变量进行比较呢?
回答 1
Stack Overflow用户
回答已采纳
发布于 2017-08-25 07:36:26
聚合酶链反应为主成分回归。这意味着您有一个因变量(在~的左手边)和许多自变量(~的右侧),就像线性回归一样。
PCR首先对自变量进行主成分分析(),然后对主成分进行因变量回归。这就是为什么在选择不同的因变量时得到不同的结果的原因。
这只有助于处理自变量的多重共线性()。因此,当您想要运行线性回归时,这项技术是有用的,但是您有自变量的多重共线性问题。它在降维任务(例如,当您没有指定的因变量时)并不有用,因为PCA是这样的。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/45873236
复制相关文章
相似问题

